基因组选择(Genomic Selection, GS)技术已成为现代作物智慧育种的核心驱动力之一,它通过全基因组分子标记高效预测个体育种值,大幅缩短育种周期。然而,当前GS模型主要依赖单核苷酸多态性(SNP)标记,其在解析复杂农艺性状遗传机制上存在一定局限。与之相比,染色体结构变异(Structural Variation, SV)——包括大片段(>50 bp)的插入、缺失、倒位和易位——通常对基因功能具有更直接的影响。启动子区的SV可调控基因表达水平,编码区的SV则可能直接改变蛋白质结构,从而主导关键表型的形成。尽管SV在部分作物GS研究中已展现出巨大潜力,但在水稻这一重要粮食作物的育种应用中,其价值尚未被充分发掘,相关研究鲜有报道。

近日,安徽农业大学农学院联合中国农业科学院作物科学研究所和河北农业大学在The Crop Journal在线发表了题为“Comprehensive comparison between structural variants and single-nucleotide polymorphism in genomic selection of rice (Oryza sativa L.)”的研究论文,系统比较了SNP与SV作为分子标记在水稻基因组选择中的预测效能,涵盖了9种主流预测模型和20个重要农艺性状。
本研究基于“3000份水稻基因组计划”中的305份高质量测序材料,整合分析了超过26,000个SVs(超过90%为缺失和易位)与180,000余个SNPs在GS中的预测效果。研究采用9种主流GS模型(包括GBLUP、多种贝叶斯模型和随机森林等),评估了单独使用SNP或者SV以及两者联合使用的预测准确度(Prediction Accuracy, PA)。结果表明,SV的整体预测准确度与SNP接近(略低),但其所需标记数量仅为SNP的约20%,计算时间平均节省53.8%—77.8%,尤其在高遗传力性状上的表现更为突出。此外,基因区域内SV的比例(45.7%)显著高于SNP(40.2%),提示SV更有可能直接关联功能相关的遗传变异。为进一步提升预测性能,研究引入全基因组关联分析(GWAS)进行标记筛选。两种标记的PA均得到显著提升,其中P<0.01被确定为SV和SNP联合筛选的最优阈值,平均PA分别提升至0.733(SV)和0.776(SNP),有效减少了噪声标记的干扰。为进一步验证基于SV的GS在实际育种中的应用价值,研究针对粒长、粒宽和千粒重这三个重要产量品质性状,分别基于SV和SNP预测了群体的基因组估计育种值(GEBVs),并筛选出排名前20的优异种质。经过连续三年的田间表型验证,发现基于SV和SNP筛选出的优异种质名单高度一致,且两组材料在实际田间表现无显著差异,充分证明利用SV能够准确筛选出具有育种潜力的优良亲本材料,展现了SV在基因组选择中的重要应用价值。
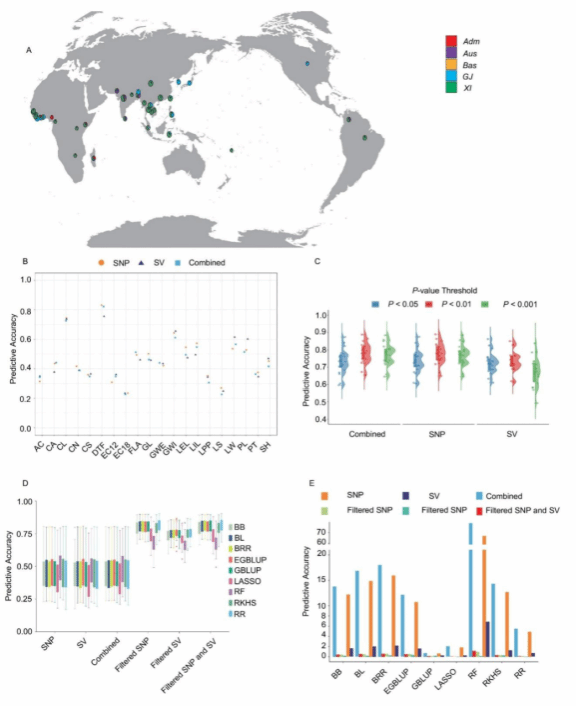
图1 基于不同标记(SV/SNP)和模型对水稻20个性状的基因组选择比较
本研究首次在水稻中对SV与SNP作为GS分子标记的性能开展了全面系统的比较分析,揭示了SV作为一种极具潜力的新型GS分子标记的重要价值。尽管SV的预测准确性略低于SNP,但其仅需约20%的标记数量即可实现相当的预测效果,显著提升了计算效率,在预测准确性与计算成本之间实现了最优平衡。研究的核心结论为育种实践亦提供了明确指导:针对高遗传力性状,育种家可优先选用SV标记,大幅缩短分析周期,加速育种进程;而对于遗传机制复杂的低遗传力性状,SNP仍是更稳健的选择。本研究所鉴定的所有SV数据及完整分析流程也已公开分享,为水稻基因功能解析、优异等位基因挖掘及高效基因组选择育种策略的开发提供了重要资源支撑。本研究亦是农学院在深化“1+5”农业科技创新联盟融合、以智慧育种支撑江淮粮仓建设方面所进行的重要实践。
安徽农业大学农学院已毕业硕士研究生梁伦平、安徽农业大学农学院青年教师张超普、在读硕士研究生余林俊为该文共同第一作者,安徽农业大学农学院黎珉副教授、中国农业科学院作物科学研究所王文生研究员和河北农业大学农学院崔彦茹副教授为共同通讯作者。安徽农业大学农学院讲席教授黎志康研究员和中国农业科学院作物科学研究所张帆研究员给予了重要指导。该研究得到安徽省自然科学基金(2408085MC058,2308085QC91)、国家自然科学基金(32301783,U21A20214)、“生物育种”国家科技重大专项(2022ZD04017)、中国农业科学院创新项目(CAAS CSIAF-202303)、中国农业科学院南繁专项(YYLH2401)等项目资助。(文图:黎珉 初审:范宇 复审:余恩 终审:王晓波)